日前�����,由淡水漁業研究中心徐跑研究員領銜的“長江重要種質資源評估與保護創新團隊”��,聯合深圳華大基因簡建波研究員團隊在洄游型刀鱭遺傳資源解析方面取得新進展��。
團隊結合牛津納米孔技術(ONT)超長和PacBio HiFi(高保真度)數據,借助高通量染色體構象捕獲技術(Hi-C),獲得了高連續性、完整性和準確性的刀鱭無間隙基因組。無間隙全基因組組裝的結果能夠解析刀鱭的全面遺傳信息���,為刀鱭的進一步分子研究提供遺傳學基礎。
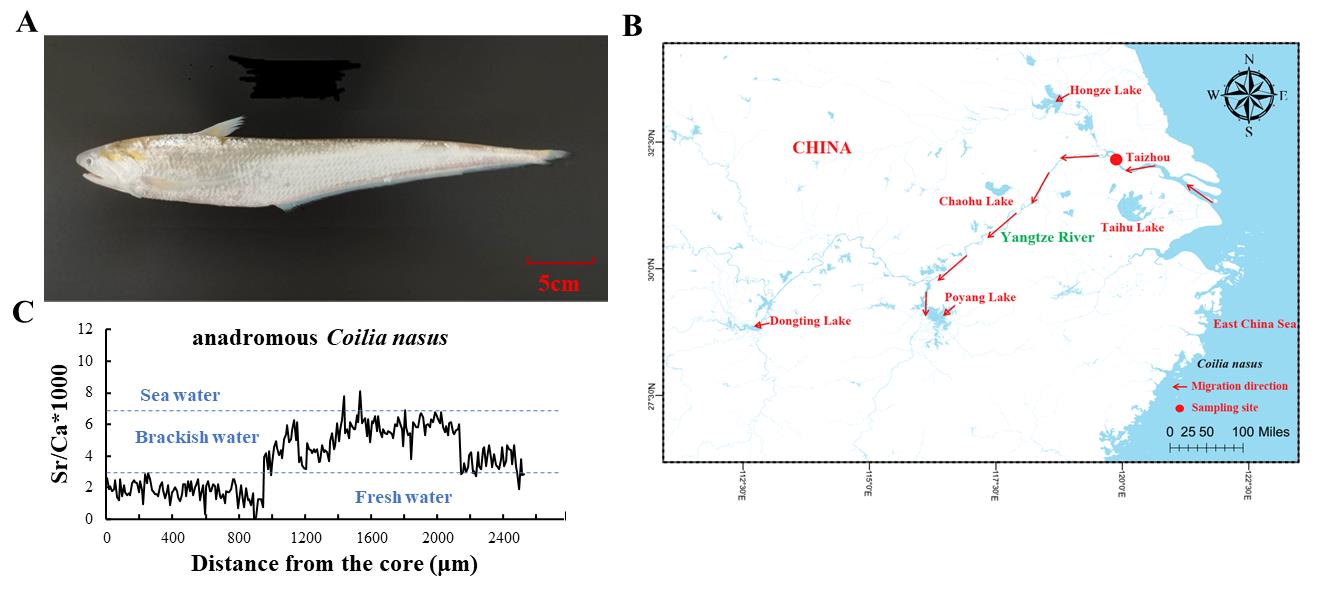
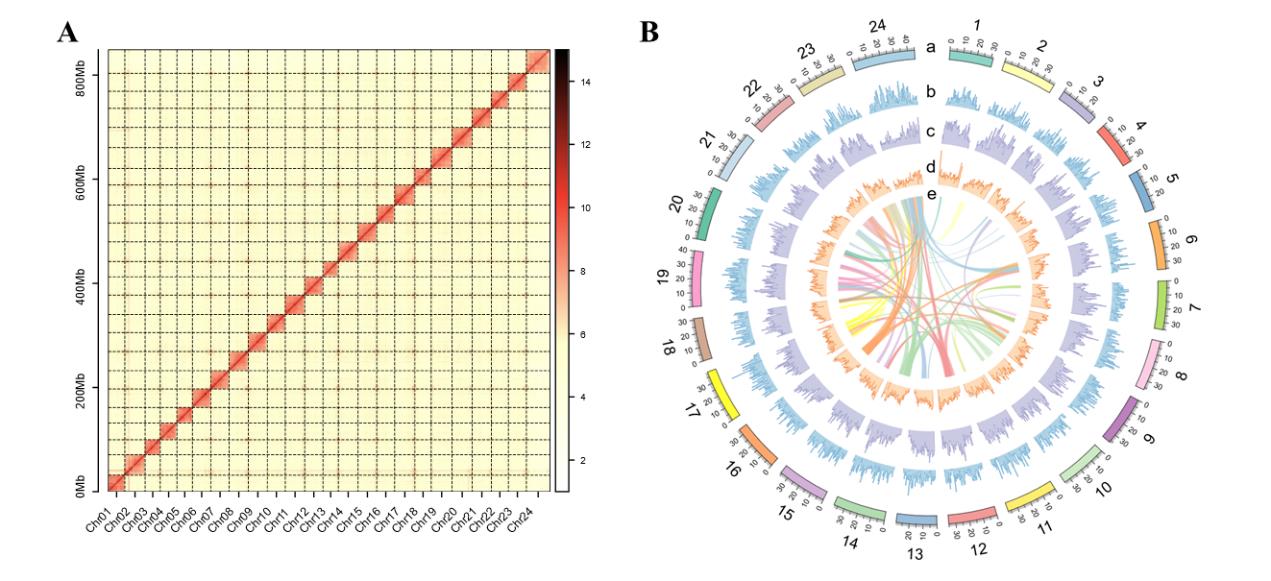
團隊對來自江蘇泰州段的洄游型刀鱭Coilia nasus進行了無間隙基因組組裝,利用PacBio HiFi(~43×)��、ONT ultra-long(~100×)及Hi-C(~100×)技術組裝得到首個0 gap的刀鱭完整基因組��。該基因組大小為851.67 Mb�����,contig N50達到35.42 Mb,BUSCO為92.5%��。注釋共獲得21971個基因���,重復序列占比為45.17%��。
相關成果論文“Gap-free genome assembly of anadromous Coilia nasus”發表在期刊《Scientific Data》上�����。南京農業大學馬鳳嬌博士��、淡水中心王銀平副研究員���、華大基因蘇碧秀博士和趙辰曦博士為共同第一作者�����,淡水中心徐跑研究員��、殷國俊研究員、劉凱研究員和華大基因簡建波研究員為通訊作者。
論文全文地址:https://www.nature.com/articles/s41597-023-02278-w
(淮河流域漁業生態保護研究中心 供稿)